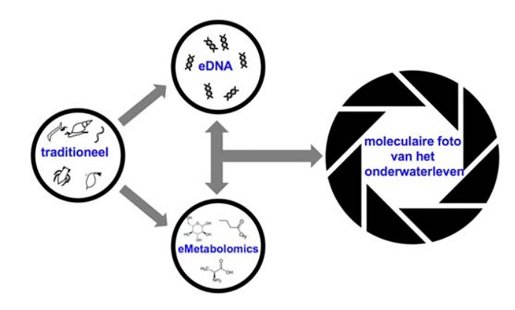
eDNA en eMetabolomics: moleculaire foto’s van het onderwaterleven
Nederland is een waterland. Schoon oppervlaktewater is belangrijk voor de natuur, landbouw en voedsel- en drinkwaterproductie en het is daarom zeer belangrijk om verstoringen daarvan goed te kunnen meten en begrijpen. Hoe eerder een verstoring van het aquatisch ecosysteem gemeten kan worden, hoe beter de mogelijkheden zijn voor waterbeheerders om het effect ervan te beperken door maatregels te nemen.
In dit project combineren wij eMetabolomics en eDNA, zodat we ‘moleculaire foto’s’ van het onderwaterleven kunnen maken die een schat aan informatie bevatten. Met behulp van deze informatie kunnen we:
-
de effecten van verstoringen eerder opsporen
-
de verstoringen beter begrijpen
-
aanknopingspunten identificeren om de verstoringen tegen te gaan
Hiertoe hebben we een consortium samengesteld waarin kennis op het gebied van de wetenschappelijke velden analytische chemie, milieukunde, ecologie en biodiversiteit, bedrijven die actief zijn in deze werkvelden en potentiële eindgebruikers zijn samengebracht. Aan de hand van twee relevante casussen zullen wij eMetabolomics en eDNA technieken ontwikkelen en toepassen.
De eerste casus is een relevante biologische verstoring door de invasieve exoot: de rode Amerikaanse rivierkreeft (Procambarus clarkii). De tweede casus een relevante chemische verstoring door het insecticide thiacloprid. Het onderzoek zal gebruik maken van nieuwe technieken op het gebied van eMetabolomics en eDNA. Met deze technieken zullen rivierkreeften in detail worden onderzocht in, onder andere, aquaria. Daarnaast zal een belangrijk deel van het onderzoek plaatsvinden in het Levend Lab, een unieke proefopstelling bestaande uit 36 slootjes waarin de invloed van thiacloprid op het aquatisch ecosysteem zal worden onderzocht.
De samenstelling van het consortium, de state-of-the-art technologie die wordt toegepast én de setting waarin het onderzoek wordt uitgevoerd maken het project zeer aantrekkelijk voor zowel studenten als docenten, waardoor doorwerking in het onderwijs gegarandeerd is.
Resultaten
Kreeften lijken niet veel effect te hebben op het ecosysteem (bacteriën, algen, diatomeeën, insecten). Wel hebben kreeften aantoonbaar effect op de aanwezigheid van bepaalde soorten macrofyten. In een geeutrofieerde/vermeste situatie lijken kreeften, boven op het effect van meststoffen, een additief effect te hebben op de aanwezigheid van bepaalde bacteriën en diatomeeën. Voor het meten van metabolieten in watersamples is het voorbewerken van de samples geoptimaliseerd, zo konden sterk geconcentreerde watersamples worden gemeten. Door optimalisatie van LC-MS en GC-MS voorbewerking en analysetechnieken konden biogene amines, aminozuren en vetzuren worden gemeten. In de watersamples uit de aquaria kon mbv de GC-MS geen specifieke hormonen van de rode rivierkreeft worden geïdentificeerd. Met de LC-MS konden meer dan 2000 stoffen worden gedetecteerd. De watersamples van het levendlab worden verder geanalyseerd mbv de LC-MS waarna deze gecombineerd worden met de eDNA resultaten.
Technieken
- Principal component analysis, partial least-squares discriminant analysis (PLSDA)
- T-tests, fold-change analysis en vulcano plotting
- Pathway enrichment analysis
- LC-MS en GC-MS
- DNA isolatie
- Agilent 1200 HPLC systeem met reversed phase kolom en een Bruker Daltonics Quadrupole Time of Flight massaspectrometer (MicrOTOF-Q MS)
- DNA sequencing
- Multivariate statistische technieken
- Metabarcoding op een Illumina MiSeq platform
- Fragmentatiespectra
- Multivariate statistiek
- eDNA analyse: soortspecifieke primer en differential display PCR
Projectinformatie
|
Type project |
RAAK-publiek |
|
Looptijd |
01-03-2019 t/m 01-01-2022 |
|
Status |
Afgerond |
|
Onderzoeksgroep(en) |
Metabolomics, Bio-informatica |
|
Projectleiding |
Peter Lindenburg (MB), Floyd Wittink |
|
Docentonderzoeker(s) |
Andre van Roon (CH), Sonja Kaal (CH) |
|
Analist(en) |
Evelyne Burgwal (CH), Nanda Koopman (CH) |
|
Student(en) |
6 studenten Chemie 4e jaars |
|
Partner(s) |
Hogeschool Leiden, Universiteit Leiden: Centrum voor Milieuwetenschappen, Universiteit Leiden: Leiden Academic Centre for Drug Research, Naturalis Biodiversity Centre, Vrije Universiteit Amsterdam: Department Animal ecology, Bureau Waardenburg, Witteveen+Bos Raadgevende ingenieurs B.V., Baseclear B.V., Bruker Nederland B.V., KWR, Wetsus, Hoogheemraadschap van Rijnland, Samenwerkingsorgaan Holland- Rijnland |


